Transcription factors are very diverse family of proteins involved in activating or repressing the transcription of a gene at a given time. Several studies using animal models demonstrated the role of transcription factor genes in craniofacial development.
ObjectiveWe aimed to investigate the association of IRF6 intron‐6 polymorphism in the non‐syndromic cleft lip with or without palate in a South Indian population.
Methods173 unrelated nonsyndromic cleft lip with or without cleft palate patients and 176 controls without clefts patients were genotyped for IRF6 rs2235375 variant by allele‐specific amplification using the KASPar single nucleotide polymorphism genotyping system. The association between interferon regulatory factor‐6 gene intron‐6 dbSNP208032210:g.G>C (rs2235375) single nucleotide polymorphism and non‐syndromic cleft lip with or without palate risk was investigated by chi‐square test.
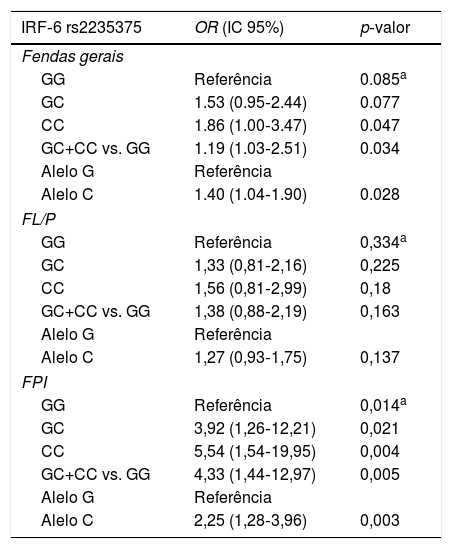
ResultsThere were significant differences in genotype or allele frequencies of rs2235375 single nucleotide polymorphism between controls and cases with non‐syndromic cleft lip with or without palate. IRF6 rs2235375 variant was significantly associated with increased risk of non‐syndromic cleft lip with or without palate in co‐dominant, dominant (OR: 1.19; 95% CI 1.03–2.51; p=0.034) and allelic models (OR: 1.40; 95% CI 1.04–1.90; p=0.028). When subset analysis was applied significantly increased risk was observed in cleft palate only group (OR dominant: 4.33; 95% CI 1.44–12.97; p=0.005).
ConclusionThese results suggest that IRF6 rs2235375 SNP play a major role in the pathogenesis and risk of developing non‐syndromic cleft lip with or without palate.
Fatores de transcrição constituem uma família de proteínas muito diversa envolvida na ativação ou repressão da transcrição de um gene, em um determinado momento. Vários estudos usando modelos animais demonstraram o papel dos genes do fator de transcrição no desenvolvimento craniofacial.
ObjetivoNosso objetivo foi investigar a associação do polimorfismo IRF6 intron‐6 na fenda labial não sindrômica com ou sem fenda palatina em uma população do sul da Índia.
MétodoUm total de 173 pacientes com fenda labial não sindrômica com ou sem fenda palatina e 176 controles sem fendas foram genotipados para a variante IRF6 rs2235375 por amplificação alelo‐específica utilizando o sistema KASPar de genotipagem de polimorfismo de nucleotídeo único. A associação entre o polimorfismo de nucleotídeo único Fator 6 Regulatório do Interferon (IRF6) intron‐6 dbSNP208032210:g.G>C (rs2235375) e o risco de fenda labial não sindrômica com ou sem fenda palatina foi investigado pelo teste qui‐quadrado.
ResultadosHouve diferenças significativas nas frequências de genótipos ou alelos do rs2235375 SNP entre controles e casos com fenda labial não sindrômica com ou sem fenda palatina. A variante IRF6 rs2235375 foi significativamente associada ao aumento do risco de fenda labial não sindrômica com ou sem fenda palatina em modelos codominantes, dominantes (OR: 1,19; IC 95%: 1,03‐2,51; p=0,034) e alélicos (OR: 1,40; IC 95%: 1,04‐1,90; p=0,028). Quando a análise do subgrupo foi realizada, um risco significativamente aumentado foi observado no grupo Fenda Palatina Isolada (OR dominante: 4,33; IC 95%: 1,44‐12,97; p=0,005).
ConclusõesEsses resultados sugerem que o polimorfismo de nucleotídeo único IRF6 rs2235375 desempenha um papel importante na patogênese e no risco de desenvolvimento de fenda labial não sindrômica com ou sem fenda palatina.
Fatores de transcrição constituem uma família de proteínas muito diversa, envolvida na ativação ou supressão da transcrição de um gene, em um determinado momento. Durante o desenvolvimento, os fatores de transcrição são responsáveis por direcionar o destino das células individuais. Várias linhas de evidência demonstraram o papel dos genes do fator de transcrição no desenvolvimento craniofacial e também as variantes desses genes desempenhando um papel crucial na etiologia da fenda labial não sindrômica com ou sem fenda palatina (FLNS/P).1,2 O fator regulatório interferon‐6 (IRF6) é um fator de transcrição que codifica o domínio de ligação ao DNA hélice –giro‐ hélice e o domínio de ligação à proteína menos conservado. Nos seres humanos, nove IRFs foram relatados e a análise da composição da sequência de aminoácidos mostrou 89% de similaridade entre IRF6 e IRF5, que desempenham um papel na ativação do interferon e na supressão tumoral.3 A hibridização in situ de embriões de ratos demonstrou que o IRF6 tem alta expressão nas bordas medianas das prateleiras palatinas emparelhadas imediatamente antes e durante a sua fusão. A expressão de IRF6 também foi detectada em folículos capilares, rugas palatinas, germes dentários, ducto tireoglosso, genitália externa e na pele de todo o corpo.4 Pesquisas recentes mostraram que os camundongos com IRF6 mutante exibem uma epiderme hiperproliferativa que não sofre diferenciação terminal, o que leva a múltiplas adesões epiteliais que podem ocluir a cavidade oral e resultar em fenda palatina.5
O Fator Regulatório Interferon‐6 (IRF6) está localizado no cromossomo 1q32.2 e é um dos genes candidatos associados com ambos os tipos de fendas sindrômicas e não sindrômicas.6–8 Além disso, vários estudos de associação do genoma inteiro, GWAS, (do inglês Genome‐Wide Association Studies) identificaram IRF6 como um locus associado com fendas orais.9,10 Esse gene contém 10 exons e, entre eles, os exons 1, 2 e 10 não são codificadores. A proteína codificadora do IRF6 contém um total de 517 aminoácidos e contém um domínio N‐terminal de ligação ao DNA hélice‐ giro‐ hélice e um domínio C‐terminal SMIR (Fator de ligação regulador de interferon). Estudos em seres humanos mostraram que alelos comuns em IRF6 eram associados à FLNS/P em diferentes populações.11
Nosso estudo anterior indicou que haplótipos de dois polimorfismos de genes IRF6 estão associados à FLNS/P.12 Neste estudo, estendemos nosso trabalho anterior para avaliar a associação entre Intron‐6 dbSNP208032210:g.G>C (rs2235375) polimorfismo de nucleotídeo único com o risco de fenda labial não sindrômica com ou sem palato em uma população do sul da Índia.
MétodoO Comitê de Ética da Instituição da Universidade Sri Ramachandra, Chennai, Índia, aprovou o projeto do estudo (Ref: IEC‐NI / II / OCT / 25/60 datado de 12.01.2012). Consentimento informado foi obtido dos pais ou responsável legal quando o paciente era menor de idade. O estudo incluiu 176 casos de FLNS/P (77 do sexo feminino e 99 do sexo masculino) e 173 controles (77 do sexo feminino e 96 do sexo masculino). Os participantes do estudo foram recrutados do Centro de Fendas e Craniofacial da Universidade Sri Ramachandra, Chennai, Índia. Dois cirurgiões avaliaram independentemente o fenótipo da fenda, e os casos com retardo mental ou quaisquer outras anomalias foram excluídos do estudo. Dos 176 casos de FLNS/ P, 104 tinham fenda labial com fenda palatina (FL/P; 76 unilateral e 28 bilaterais), 40 tinham apenas fenda labial (FLI) e 29 apenas fenda palatina isolada (FPI). Ambos os casos de FLI e FPI eram unilaterais e nenhum dos pacientes tinha parentes afetados. Indivíduos pareados por idade e gênero sem histórico familiar de fenda foram recrutados como controles. Foi coletada uma amostra de sangue periférico de 3mL de cada indivíduo e o DNA foi extraído utilizando‐se um procedimento padrão.13 A genotipagem do IRF6 rs2235375 SNP foi realizada pela KBioscience usando KASPar.14,15 A genotipagem de polimorfismo de nucleotídeo único através do sistema KASPar envolve PCR alelo‐específica utilizando os oligonucleotídeos FRET quencher cassette (tabela 1). Com base na fluorescência obtida, os dados de chamada de alelos foram visualizados graficamente como um gráfico de dispersão usando o SNPViewer (http://www.lgcgenomics.com). O equilíbrio de Hardy‐Weinberg (EHW) foi avaliado em ambos os casos e grupos de controle usando o teste do qui‐quadrado. As frequências alélicas foram estimadas pelo método de contagem de genes.16 A comparação das frequências de genótipos e alelos entre os casos e os grupos de controle foi analisada pelo teste do qui‐quadrado. O odds ratio e os intervalos de confiança de 95% foram calculados utilizando genótipos e alelos de tipo selvagem como grupo de referência.
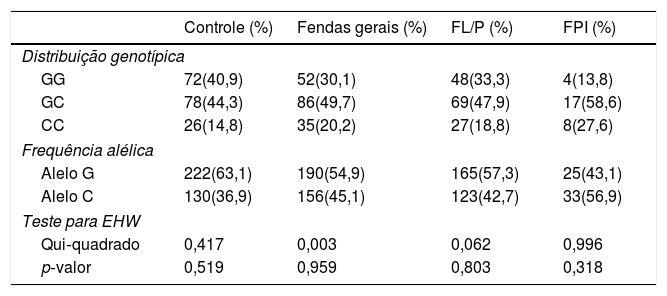
ResultadosA distribuição dos genótipos e alelos da variante IRF6 rs2235375 em ambos os casos e grupos de FLNS/P são apresentados na tabela 2. As proporções de genótipos foram 30,1% GG, 49,7% GC, 20,2% CC nos casos e 40,9% GG, 44,3% GC, e 14,8% CC nos controles. A frequência do alelo C foi 45,1% nos casos e 36,9% nos controles. As frequências do genótipo IRF6 rs2235375 eram distribuídas de acordo com o equilíbrio de Hardy‐Weinberg entre os controles (p = 0,519). Diferença significante nas frequências de alelos foi encontrada entre os grupos controle e os FLNS/P (tabela 3). Odds ratio e IC de 95% foram calculados para avaliar o risco relativo de fendas orais ao comparar as frequências genotípicas de casos e controles em modelos codominantes, dominantes e alélicos (tabela 3). Um risco significantemente maior de FLNS/P foi encontrado para o genótipo homozigoto (CC vs. GG; OR = 1,86; IC 95%: 1,0‐3,47; p = 0,047). Um risco aumentado de FLNS/P também foi encontrado em modelos dominantes (GC + CC vs. GG; OR = 1,19; IC 95% 1,03‐2,51; p = 0,034) e alélicos (C vs. G; OR = 1,40; IC 95%; 1,04 ‐1.90; p = 0,028). Na análise de subgrupos, a variante IRF6 rs2235375 mostrou risco significantemente aumentado de FPI em três modelos diferentes (tabela 3).
Distribuição de genótipos e frequências de alelos do IRF6 rs2235375 SNP em fenda labial e palatina
| Controle (%) | Fendas gerais (%) | FL/P (%) | FPI (%) | |
|---|---|---|---|---|
| Distribuição genotípica | ||||
| GG | 72(40,9) | 52(30,1) | 48(33,3) | 4(13,8) |
| GC | 78(44,3) | 86(49,7) | 69(47,9) | 17(58,6) |
| CC | 26(14,8) | 35(20,2) | 27(18,8) | 8(27,6) |
| Frequência alélica | ||||
| Alelo G | 222(63,1) | 190(54,9) | 165(57,3) | 25(43,1) |
| Alelo C | 130(36,9) | 156(45,1) | 123(42,7) | 33(56,9) |
| Teste para EHW | ||||
| Qui‐quadrado | 0,417 | 0,003 | 0,062 | 0,996 |
| p‐valor | 0,519 | 0,959 | 0,803 | 0,318 |
FL/P, Fenda Labial e Palatina; FPI, Fenda Palatina Isolada; EHW, equilíbrio de Hardy‐Weinberg.
Resultados dos testes de associação com IRF6 rs2235375 SNP em fenda labial e palatina
| IRF‐6 rs2235375 | OR (IC 95%) | p‐valor |
|---|---|---|
| Fendas gerais | ||
| GG | Referência | 0.085a |
| GC | 1.53 (0.95‐2.44) | 0.077 |
| CC | 1.86 (1.00‐3.47) | 0.047 |
| GC+CC vs. GG | 1.19 (1.03‐2.51) | 0.034 |
| Alelo G | Referência | |
| Alelo C | 1.40 (1.04‐1.90) | 0.028 |
| FL/P | ||
| GG | Referência | 0,334a |
| GC | 1,33 (0,81‐2,16) | 0,225 |
| CC | 1,56 (0,81‐2,99) | 0,18 |
| GC+CC vs. GG | 1,38 (0,88‐2,19) | 0,163 |
| Alelo G | Referência | |
| Alelo C | 1,27 (0,93‐1,75) | 0,137 |
| FPI | ||
| GG | Referência | 0,014a |
| GC | 3,92 (1,26‐12,21) | 0,021 |
| CC | 5,54 (1,54‐19,95) | 0,004 |
| GC+CC vs. GG | 4,33 (1,44‐12,97) | 0,005 |
| Alelo G | Referência | |
| Alelo C | 2,25 (1,28‐3,96) | 0,003 |
IRF6, fator regulador de interferon 6; OR, Odds Ratio; IC, Intervalo de Confiança; FL/P, Fenda Labial e Palatina; FPI, Fenda Palatina Isolada.
Nossos achados mostram claramente que o IRF6 rs2235375 desempenha um papel predominante no desenvolvimento de FLNS/P. Este estudo fornece evidências confirmatórias para as variantes que foram relatadas anteriormente, como sendo associadas à FLNS/P. O papel do IRF6 foi identificado durante o desenvolvimento embrionário, mas sua função reguladora ainda precisa ser esclarecida.5,17 No momento da fusão do palato, ocorre a degradação do epitélio da borda medial (EBM) e o aumento da expressão do IRF6 foi observado na EBM durante este processo.18,19 Os padrões de expressão do desenvolvimento de ortólogos do IRF6 em camundongos e pintinhos revelaram presença de expressão do IRF6 na fusão do ectoderma formando o lábio superior e o palato primário em ambos os ratos e pintinhos, mas apenas no desenvolvimento do palato secundário do camundongo.20
Uma meta‐análise de 20 estudos de caso‐controle publicados demonstrou que rs2235371 e rs642961 são antagonistas entre si na atribuição do risco de FLNS /P.21 O alelo “A” de um polimorfismo funcional (rs2235371; 820G > A) contribuiu para um aumento do risco de FLNS/P na população chinesa.22 De maneira inversa, o alelo “G” foi sobre‐transmitido em poucos estudos.11 Poucas análises baseadas em haplótipos confirmaram que o rs2235371 estava associado à FLNS / P.23–25 Em contraste com isso, o SNP rs2235371, não mostrou associação com fendas orais em algumas populações.26–29 Demonstramos anteriormente que o alelo G do IRF6 rs2235371 é sobre‐transmitido em pacientes Indianos com fendas, mas o genótipo 820GG contribuiu apenas para um risco menor.30 Há poucos estudos de associação disponíveis para o SNP rs642961, mas os resultados foram inconsistentes. Foi observada associação significante entre rs642961 e FLNS/ P.26,31–34 Em contraste com os estudos acima mencionados, nenhuma associação foi relatada por vários estudos.29,35–37
Os estudos de associação do genoma inteiro, e seus estudos de replicação de seguimento estabeleceram o IRF6 como um dos genes candidatos para a patogênese da FLNS/ P.38 O polimorfismo analisado nesse estudo (rs2235375) está localizado no intron‐6 do IRF6. Este polimorfismo demonstrou uma associação positiva entre essa variante e FLNS/ P em várias populações, como a italiana,7 europeia‐americana,25 norueguesa,39 chilena,28 chinesa40 e brasileira.41
ConclusãoEm conclusão, os resultados do presente estudo indicam que o polimorfismo IRF6 rs2235375 está associado à FLNS/P em uma população do sul da Índia.
Conflitos de interesseOs autores declaram não haver conflitos de interesse.
L.V.K.S. Bhaskar agradece ao Conselho Indiano de Pesquisa Média (Indian Council of Medical Research ‐ ICMR) pela ajuda financeira recebida, e ao Governo da Índia (Projeto Ref. n° 56/15/2007‐BMS e n° 45/3/2013‐Hum/BMS).
Como citar este artigo: Gurramkonda VB, Syed AH, Murthy J, Lakkakula BV. IRF6 rs2235375 single nucleotide polymorphism is associated with isolated non‐syndromic cleft palate but not with cleft lip with or without palate in South Indian population. Braz J Otorhinolaryngol. 2018;84:473–7.
A revisão por pares é da responsabilidade da Associação Brasileira de Otorrinolaringologia e Cirurgia Cérvico‐Facial.